1 Department of Clinical Sciences, Lund University, 20502 Malmö, Sweden
2 Infection Medicine, Department of Clinical Sciences, Lund University, 22362 Lund, Sweden
Συγγραφέας στον οποίο πρέπει να απευθύνεται η αλληλογραφία.
Ακαδημαϊκή επιμέλεια: Stephen Malnick
Curr. Θέματα Μολ. Biol. 2022 , 44 (3), 1115-1126; https://doi.org/10.3390/cimb44030073
Λήψη: 18 Ιανουαρίου 2022 / Αναθεώρηση: 19 Φεβρουαρίου 2022 / Αποδοχή: 23 Φεβρουαρίου 2022 / Δημοσιεύθηκε: 25 Φεβρουαρίου 2022
(Αυτό το άρθρο ανήκει στο Θέμα Κλινική, Μεταφραστική και Βασική Έρευνα για τις ασθένειες του ήπατος )
Περίληψη
Οι προκλινικές μελέτες του εμβολίου mRNA του COVID-19 BNT162b2, που αναπτύχθηκε από την Pfizer και τη BioNTech, έδειξαν αναστρέψιμες ηπατικές επιδράσεις σε ζώα που έλαβαν την ένεση BNT162b2. Επιπλέον, μια πρόσφατη μελέτη έδειξε ότι το RNA του SARS-CoV-2 μπορεί να αντιστραφεί και να ενσωματωθεί στο γονιδίωμα των ανθρώπινων κυττάρων. Σε αυτή τη μελέτη, διερευνήσαμε την επίδραση του BNT162b2 στην κυτταρική σειρά ανθρώπινου ήπατος Huh7 in vitro. Τα κύτταρα Huh7 εκτέθηκαν σε BNT162b2 και πραγματοποιήθηκε ποσοτική PCR σε RNA που εκχυλίστηκε από τα κύτταρα. Ανιχνεύσαμε υψηλά επίπεδα BNT162b2 σε κύτταρα Huh7 και αλλαγές στη γονιδιακή έκφραση του μακράς διάσπαρτου πυρηνικού στοιχείου-1 (LINE-1), που είναι μια ενδογενής αντίστροφη μεταγραφάση. Η ανοσοϊστοχημεία που χρησιμοποιεί δέσμευση αντισώματος με LINE-1 ανοιχτό πλαίσιο ανάγνωσης-1 πρωτεΐνη δέσμευσης RNA (ORFp1) σε κύτταρα Huh7 που υποβλήθηκαν σε αγωγή με BNT162b2 έδειξε αυξημένη κατανομή πυρήνα της LINE-1. Η PCR σε γονιδιωματικό DNA κυττάρων Huh7 που εκτέθηκαν σε BNT162b2 ενίσχυσε την αλληλουχία DNA μοναδική για το BNT162b2. Τα αποτελέσματά μας υποδεικνύουν γρήγορη πρόσληψη του BNT162b2 στην ανθρώπινη κυτταρική σειρά του ήπατος Huh7, που οδηγεί σε αλλαγές στην έκφραση και κατανομή της LINE-1. Δείχνουμε επίσης ότι το mRNA του BNT162b2 μεταγράφεται αντίστροφα ενδοκυτταρικά στο DNA σε μόλις 6 ώρες μετά την έκθεση στο BNT162b2.
1. Εισαγωγή
Η νόσος του κορωνοϊού 2019 (COVID-19) που προκαλείται από σοβαρό οξύ αναπνευστικό σύνδρομο Ο κορωνοϊός 2 (SARS-CoV-2) ανακοινώθηκε από τον Παγκόσμιο Οργανισμό Υγείας (ΠΟΥ) ως παγκόσμια πανδημία στις 11 Μαρτίου 2020 και εμφανίστηκε ως καταστροφική κρίση υγείας. Από τον Φεβρουάριο του 2022, ο COVID-19 έχει οδηγήσει σε περισσότερα από 430 εκατομμύρια αναφερόμενα κρούσματα μόλυνσης και 5,9 εκατομμύρια θανάτους παγκοσμίως [ 1 ]. Απαιτούνται επειγόντως αποτελεσματικά και ασφαλή εμβόλια για τη μείωση των ποσοστών νοσηρότητας και θνησιμότητας που σχετίζονται με τον COVID-19.
Έχουν αναπτυχθεί αρκετά εμβόλια για τον COVID-19, με ιδιαίτερη έμφαση στα εμβόλια mRNA (από την Pfizer-BioNTech και τη Moderna), στα εμβόλια ανασυνδυασμένου αδενοϊικού φορέα με ελαττωματικά αντιγραφή (από τους Janssen-Johnson and Johnson, Astra-Zeneca, Sputnik-V και CanSino ), και αδρανοποιημένα εμβόλια (από Sinopharm, Bharat Biotech και Sinovac). Το εμβόλιο mRNA έχει τα πλεονεκτήματα ότι είναι ευέλικτο και αποτελεσματικό στο σχεδιασμό και την κατασκευή ανοσογόνου, και επί του παρόντος, πολλά υποψήφια εμβόλια βρίσκονται σε διάφορα στάδια ανάπτυξης και εφαρμογής.
Συγκεκριμένα, το εμβόλιο COVID-19 mRNA BNT162b2 που αναπτύχθηκε από την Pfizer και τη BioNTech έχει αξιολογηθεί σε επιτυχημένες κλινικές δοκιμές [ 2 , 3 , 4 ] και έχει χορηγηθεί σε εθνικές εκστρατείες εμβολιασμού για τον COVID-19 σε διάφορες περιοχές σε όλο τον κόσμο [ 5 , 6 , 7 , 8 ].
Το BNT162b2 είναι ένα εμβόλιο RNA τροποποιημένο με νουκλεοσίδια (modRNA) ενθυλακωμένο με νανοσωματίδια λιπιδίων (LNP) και κωδικοποιεί την πρωτεΐνη ακίδας (S) SARS-CoV-2 πλήρους μήκους, τροποποιημένη από δύο μεταλλάξεις προλίνης για να εξασφαλίσει αντιγονικά βέλτιστη διαμόρφωση πριν από τη σύντηξη , που μιμείται τον άθικτο ιό για να προκαλέσει αντισώματα εξουδετέρωσης του ιού [ 3 ].
Σε συμφωνία με τυχαιοποιημένες κλινικές δοκιμές, το BNT162b2 έδειξε υψηλή αποτελεσματικότητα σε ένα ευρύ φάσμα αποτελεσμάτων που σχετίζονται με τον COVID-19 σε πραγματικό περιβάλλον [ 5 ]. Ωστόσο, εξακολουθούν να υπάρχουν πολλές προκλήσεις, συμπεριλαμβανομένης της παρακολούθησης για μακροπρόθεσμη ασφάλεια και αποτελεσματικότητα του εμβολίου. Αυτό απαιτεί περαιτέρω αξιολόγηση και έρευνες. Το προφίλ ασφάλειας του BNT162b2 είναι προς το παρόν διαθέσιμο μόνο από βραχυπρόθεσμες κλινικές μελέτες. έχουν αναφερθεί, όπως περικαρδίτιδα, αρρυθμία, εν τω βάθει φλεβική θρόμβωση, πνευμονική εμβολή 4 , 9 , 10 , 21,4,31 αιμορραγία BNT162b2 θρομβοπενία [ μυοκαρδίου και έμφραγμα του , ενδοκρανιακή , 17 , 18 , 19 , 20 ]. Υπάρχουν επίσης μελέτες που αναφέρουν ανεπιθύμητες ενέργειες που παρατηρήθηκαν σε άλλους τύπους εμβολίων [ 21 , 22 , 23 , 24 ]. Για την καλύτερη κατανόηση των μηχανισμών στους οποίους βασίζονται οι ανεπιθύμητες ενέργειες που σχετίζονται με το εμβόλιο, απαιτούνται κλινικές έρευνες καθώς και κυτταρικές και μοριακές αναλύσεις.
Μια πρόσφατη μελέτη έδειξε ότι τα RNA του SARS-CoV-2 μπορούν να μεταγραφούν αντίστροφα και να ενσωματωθούν στο γονιδίωμα των ανθρώπινων κυττάρων [ 25 ]. Αυτό γεννά το ερώτημα εάν αυτό μπορεί να συμβεί και με το BNT162b2, το οποίο κωδικοποιεί μερικό RNA του SARS-CoV-2. Στα φαρμακοκινητικά δεδομένα που παρέχονται από την Pfizer στον Ευρωπαϊκό Οργανισμό Φαρμάκων (EMA), η βιοκατανομή του BNT162b2 μελετήθηκε σε ποντίκια και αρουραίους με ενδομυϊκή ένεση με ραδιοσημασμένο LNP και λουσιφεράση modRNA. Η ραδιενέργεια ανιχνεύθηκε στους περισσότερους ιστούς από το πρώτο χρονικό σημείο (0,25 ώρες) και τα αποτελέσματα έδειξαν ότι το σημείο της ένεσης και το ήπαρ ήταν οι κύριες θέσεις κατανομής, με μέγιστες συγκεντρώσεις που παρατηρήθηκαν στις 8-48 ώρες μετά τη δόση [ 26 ]. Επιπλέον, σε ζώα που έλαβαν την ένεση BNT162b2, παρατηρήθηκαν αναστρέψιμες ηπατικές επιδράσεις, συμπεριλαμβανομένης της διόγκωσης του ήπατος, της δημιουργίας κενοτοπίων, των αυξημένων επιπέδων γ-γλουταμυλ τρανσφεράσης (γGT) και των αυξημένων επιπέδων ασπαρτικής τρανσαμινάσης (AST) και αλκαλικής φωσφατάσης (ALP) [ 26 ]. Παροδικές ηπατικές επιδράσεις που προκαλούνται από συστήματα χορήγησης LNP έχουν αναφερθεί στο παρελθόν [ 27 , 28 , 29 , 30 ], ωστόσο, έχει επίσης αποδειχθεί ότι το κενό LNP χωρίς modRNA από μόνο του δεν εισάγει καμία σημαντική ηπατική βλάβη [ 27 ]. Επομένως, σε αυτή τη μελέτη, στοχεύουμε να εξετάσουμε την επίδραση του BNT162b2 σε μια ανθρώπινη κυτταρική σειρά ήπατος in vitro και να διερευνήσουμε εάν το BNT162b2 μπορεί να μεταγραφεί αντίστροφα στο DNA μέσω ενδογενών μηχανισμών.
2. Υλικά και μέθοδοι
2.1. Κυτταρικής καλλιέργειας
Τα κύτταρα Huh7 (JCRB Cell Bank, Osaka, Japan) καλλιεργήθηκαν σε 37 °C σε 5% CO 2 με μέσο DMEM (HyClone, HYCLSH30243.01) συμπληρωμένο με 10% ( v / v ) εμβρυϊκό βόειο ορό (Sigma-Aldrich, F7524 -500ML, Burlington, MA, ΗΠΑ) και 1% ( v / v ) πενικιλλίνη-στρεπτομυκίνη (HyClone, SV30010, Logan, UT, USA). Για την επεξεργασία BNT162b2, κύτταρα Huh7 σπάρθηκαν με πυκνότητα 200.000 κυττάρων/φρεάτιο σε πλάκες 24 φρεατίων. Το εμβόλιο mRNA BNT162b2 (Pfizer BioNTech, Νέα Υόρκη, Νέα Υόρκη, ΗΠΑ) αραιώθηκε με στείρα ένεση χλωριούχου νατρίου 0,9%, USP σε τελική συγκέντρωση 100 μg/mL όπως περιγράφεται στις οδηγίες του κατασκευαστή [ 31 ]. Το εναιώρημα BNT162b2 προστέθηκε στη συνέχεια σε μέσα κυτταροκαλλιέργειας για να φτάσει σε τελικές συγκεντρώσεις 0,5, 1,0 ή 2,0 μg/mL. Τα κύτταρα Huh7 επωάστηκαν με ή χωρίς BNT162b2 για 6, 24 και 48 ώρες. Τα κύτταρα πλύθηκαν καλά με PBS και συλλέχθηκαν με θρυψινοποίηση και αποθηκεύτηκαν στους -80 °C μέχρι περαιτέρω χρήση.
2.2. RT-QPCR σε πραγματικό χρόνο
Το RNA από τα κύτταρα εκχυλίστηκε με RNeasy Plus Mini Kit (Qiagen, 74134, Hilden, Γερμανία) σύμφωνα με το πρωτόκολλο του κατασκευαστή. Η RT-PCR πραγματοποιήθηκε χρησιμοποιώντας κιτ σύνθεσης cDNA First Strand RevertAid (Thermo Fisher Scientific, K1622, Waltham, MA, USA) σύμφωνα με το πρωτόκολλο του κατασκευαστή. Πραγματοποιήθηκε qPCR σε πραγματικό χρόνο χρησιμοποιώντας Maxima SYBR Green/ROX qPCR Master Mix (Thermo Fisher Scientific, K0222, Waltham, MA, USA) με εκκινητές για BNT162b2, LINE-1 και γονίδια housekeeping ACTB και GAPDH ( Πίνακας 1 ).
Τραπέζι 1. Αλληλουχίες εκκινητών RT-qPCR και PCR.
2.3. Ανοσοφθορισμός χρώση και ομοεστιακή απεικόνιση
Τα κύτταρα Huh7 καλλιεργήθηκαν σε πλακίδια οκτώ θαλάμων (LAB-TEK, 154534, Santa Cruz, CA, USA) με πυκνότητα 40.000 κυττάρων/φρεάτιο, με ή χωρίς BNT162b2 (0,5, 1 ή 2 μg/mL) για 6 ώρες. Η ανοσοϊστοχημεία πραγματοποιήθηκε με τη χρήση πρωτογενούς αντισώματος anti-LINE-1 ORF1p μονοκλωνικού αντισώματος ποντικού (Merck, 3574308, Kenilworth, NJ, USA), δευτερογενούς αντισώματος Cy3 Donkey anti-mouse (Jackson ImmunoResearch, West Grove, PA, USA) και Hoechst (Life technology, 34850, Carlsbad, CA, USA), ακολουθώντας το πρωτόκολλο της Thermo Fisher (Waltham, MA, USA). Λήφθηκαν δύο εικόνες ανά συνθήκη χρησιμοποιώντας ένα Zeiss LSM 800 και έναν αντικειμενικό εμβάπτισης λαδιού 63Χ και η ένταση χρώσης ποσοτικοποιήθηκε στην επιμέρους περιοχή ολόκληρου του κυττάρου και στην περιοχή του πυρήνα σε 15 κύτταρα ανά εικόνα με ImageJ 1.53c. Η ένταση χρώσης LINE-1 για το κυτοσόλιο υπολογίστηκε αφαιρώντας την ένταση του πυρήνα από αυτή ολόκληρου του κυττάρου. Σε όλες τις εικόνες των κελιών εκχωρήθηκε ένας τυχαίος αριθμός για να αποφευχθεί η μεροληψία. Για τη σήμανση των πυρήνων (που προσδιορίζονται με τη χρώση Hoechst) και των ολόκληρων κυττάρων (που καθορίζονται από τα όρια του φθορισμού LINE-1), χρησιμοποιήθηκε το εργαλείο επιλογής Freehand. Στη συνέχεια μετρήθηκαν αυτές οι περιοχές και η μέση ένταση χρησιμοποιήθηκε για τη σύγκριση των ομάδων.
2.4. Καθαρισμός γονιδιωματικού DNA, ενίσχυση PCR, καθαρισμός γέλης αγαρόζης και προσδιορισμός αλληλουχίας Sanger
Το γονιδιωματικό DNA εκχυλίστηκε από σφαιρίδια κυττάρων με ρυθμιστικό PBND (10 mM Tris-HCl ρΗ 8,3, 50 mM KCl, 2,5 mM MgCl2, 0,45% NP-40, 0,45% Tween-20) σύμφωνα με το πρωτόκολλο που περιγράφηκε προηγουμένως [ 32 ]. Για την απομάκρυνση του υπολειμματικού RNA από το παρασκεύασμα DNA, RNase (100 μg/mL, Qiagen, Hilden, Γερμανία) προστέθηκε στο παρασκεύασμα DNA και επωάστηκε στους 37 °C για 3 ώρες, ακολουθούμενο από 5 λεπτά στους 95 °C. Στη συνέχεια πραγματοποιήθηκε η PCR χρησιμοποιώντας εκκινητές που στοχεύουν το BNT162b2 (οι αλληλουχίες φαίνονται στον Πίνακα 1 ), με το ακόλουθο πρόγραμμα: 5 λεπτά στους 95 °C, 35 κύκλοι στους 95 °C για 30 δευτερόλεπτα, 58 °C για 30 δευτερόλεπτα και 72 °C για 1 λεπτό? Τέλος, 72 °C για 5 λεπτά και 12 °C για 5 λεπτά. Τα προϊόντα PCR χρησιμοποιήθηκαν σε β / ο πήκτωμα αγαρόζης Οι ζώνες που αντιστοιχούν στα αμπλικόνια του αναμενόμενου μεγέθους (444 bps) κόπηκαν και το DNA εκχυλίστηκε χρησιμοποιώντας το κιτ καθαρισμού QIAquick PCR (Qiagen, 28104, Hilden, Γερμανία), ακολουθώντας τις οδηγίες του κατασκευαστή. Η αλληλουχία του ενισχυτικού DNA επαληθεύτηκε με προσδιορισμό αλληλουχίας Sanger (Eurofins Genomics, Ebersberg, Γερμανία).
Στατιστική
-test Student t και ANOVA. Τα δεδομένα εκφράζονται ως μέσος όρος ± SEM ή ± SD. διαφορές με p < 0,05 θεωρούνται σημαντικές.
2.5. Ηθικές Δηλώσεις
Η κυτταρική σειρά Huh7 ελήφθη από την Japanese Collection of Research Bioresources (JCRB) Cell Bank.
3. Αποτελέσματα
3.1. Το BNT162b2 εισέρχεται σε κύτταρα ανθρώπινης ηπατικής γραμμής Huh7 σε υψηλή απόδοση
Για να προσδιορίσουμε εάν το BNT162b2 εισέρχεται σε ανθρώπινα ηπατικά κύτταρα, εκθέσαμε την ανθρώπινη ηπατική κυτταρική σειρά Huh7 σε BNT162b2. Σε μια προηγούμενη μελέτη σχετικά με την κινητική πρόσληψης της παροχής LNP σε κύτταρα Huh7, η μέγιστη βιολογική αποτελεσματικότητα του LNP παρατηρήθηκε μεταξύ 4-7 ωρών [ 33 ]. Επομένως, στη μελέτη μας, τα κύτταρα Huh7 καλλιεργήθηκαν με ή χωρίς αυξανόμενες συγκεντρώσεις BNT162b2 (0,5, 1,0 και 2,0 μg/mL) για 6, 24 και 48 ώρες. RNA εξήχθη από κύτταρα και διεξήχθη αλυσιδωτή αντίδραση πολυμεράσης ποσοτικής αντίστροφης μεταγραφής σε πραγματικό χρόνο (RT-qPCR) χρησιμοποιώντας εκκινητές που στοχεύουν την αλληλουχία BNT162b2, όπως απεικονίζεται στο Σχήμα 1 . Η πλήρης αλληλουχία του BNT162b2 είναι δημόσια διαθέσιμη [ 34 ] και περιέχει ένα καπάκι δύο νουκλεοτιδίων. 5′- αμετάφραστη περιοχή (UTR) που ενσωματώνει το 5′ -UTR ενός γονιδίου ανθρώπινης α-σφαιρίνης. την πλήρους μήκους πρωτεΐνη SARS-CoV-2 S με δύο μεταλλάξεις προλίνης. 3′-UTR που ενσωματώνει το ανθρώπινο μιτοχονδριακό τμήμα 12S rRNA (mtRNR1) και το ανθρώπινο τμήμα γονιδίου AES/TLE5 με δύο μεταλλάξεις C→U. πολυ(Α) ουρά. Λεπτομερής ανάλυση της αλληλουχίας πρωτεΐνης S στο BNT162b2 αποκάλυψε 124 αλληλουχίες που είναι 100% πανομοιότυπες με τις αλληλουχίες ανθρώπινου γονιδιώματος και τρεις αλληλουχίες με μόνο ένα νουκλεοτίδιο (nt) αναντιστοιχία σε 19-26 nts ( Πίνακας S1, βλέπε Συμπληρωματικά Υλικά ). Για να ανιχνεύσουμε το επίπεδο RNA BNT162b2, σχεδιάσαμε εκκινητές με εμπρόσθιο εκκινητή που βρίσκεται σε περιοχές πρωτεΐνης SARS-CoV-2 S και αντίστροφο εκκινητή σε 3′-UTR, που επιτρέπει την ανίχνευση του αμπλικονίου PCR μοναδικό για το BNT162b2 χωρίς μη ειδική δέσμευση των εκκινητών με τις ανθρώπινες γονιδιωματικές περιοχές .
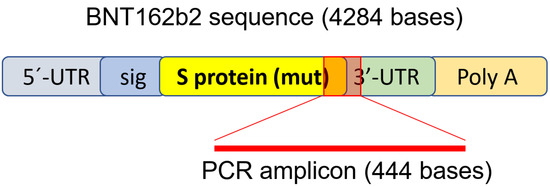
Φιγούρα 1. Σετ εκκινητών PCR που χρησιμοποιείται για την ανίχνευση του επιπέδου mRNA και την αντίστροφη μεταγραφή του BNT162b2. Η απεικόνιση του BNT162b2 προσαρμόστηκε από βιβλιογραφία που περιγράφηκε προηγουμένως [ 34 ].
Τα αποτελέσματα RT-qPCR έδειξαν ότι τα κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με BNT162b2 είχαν υψηλά επίπεδα mRNA BNT162b2 σε σχέση με τα γονίδια οικιακής φροντίδας στις 6, 24 και 48 ώρες ( Σχήμα 2 , που παρουσιάζεται σε καταγεγραμμένο 2 -ΔΔCT λόγω εξαιρετικά υψηλών επιπέδων). Οι τρεις συγκεντρώσεις BNT162b2 οδήγησαν σε παρόμοια ενδοκυτταρικά επίπεδα mRNA BNT162b2 σε διαφορετικά χρονικά σημεία, εκτός από το ότι η σημαντική διαφορά μεταξύ 1,0 και 2,0 μg/mL παρατηρήθηκε στις 48 ώρες. Τα επίπεδα mRNA του BNT162b2 μειώθηκαν σημαντικά στις 24 ώρες σε σύγκριση με τις 6 ώρες, αλλά αυξήθηκαν ξανά στις 48 ώρες.
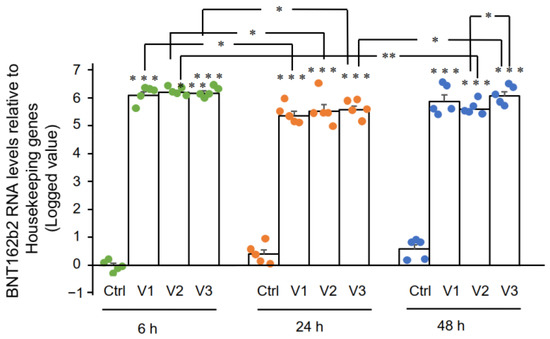
Σχήμα 2. Επίπεδα mRNA BNT162b2 σε κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με BNT162b2. Τα κύτταρα Huh7 υποβλήθηκαν σε επεξεργασία χωρίς (Ctrl) ή με 0,5 (V1), 1 (V2) και 2 μg/mL (V3) BNT162b2 για 6 (πράσινες κουκκίδες), 24 (πορτοκαλί κουκκίδες) και 48 ώρες (μπλε κουκκίδες) . Το RNA καθαρίστηκε και εκτελέστηκε qPCR χρησιμοποιώντας εκκινητές που στοχεύουν το BNT162b2. Τα επίπεδα RNA του BNT162b2 παρουσιάζονται ως καταγεγραμμένες τιμές 2 -ΔΔCT σε σχέση με τα γονίδια οικιακής χρήσης GAPDH και ACTB . Τα αποτελέσματα προέρχονται από πέντε ανεξάρτητα πειράματα ( n = 5). Οι διαφορές μεταξύ των αντίστοιχων ομάδων αναλύθηκαν με τη χρήση t-test Student δύο ουρών . Τα δεδομένα εκφράζονται ως μέσος όρος ± SEM. (* p < 0,05, ** p < 0,01, *** p < 0,001 έναντι του αντίστοιχου ελέγχου σε κάθε χρονικό σημείο ή όπως υποδεικνύεται).
3.2. Επίδραση του BNT162b2 σε Ανθρώπινη Ενδογενή Αντίστροφη Μεταγραφάση Μακράς Διάσπαρτου Πυρηνικού Στοιχείου-1 (LINE-1)
Εδώ εξετάσαμε την επίδραση του BNT162b2 στην LINE-1 . Η RT-qPCR πραγματοποιήθηκε σε RNA καθαρισμένο από κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με BNT162b2 (0, 0,5, 1,0 και 2,0 μg/mL) για 6, 24 και 48 ώρες, χρησιμοποιώντας εκκινητές που στοχεύουν τη LINE-1 . Σημαντικά αυξημένη LINE-1 σε σύγκριση με τον έλεγχο παρατηρήθηκε στις 6 ώρες κατά 2,0 μg/mL BNT162b2, ενώ χαμηλότερες συγκεντρώσεις BNT162b2 μείωσαν LINE-1 σε όλα τα χρονικά σημεία ( Εικόνα 3 ).
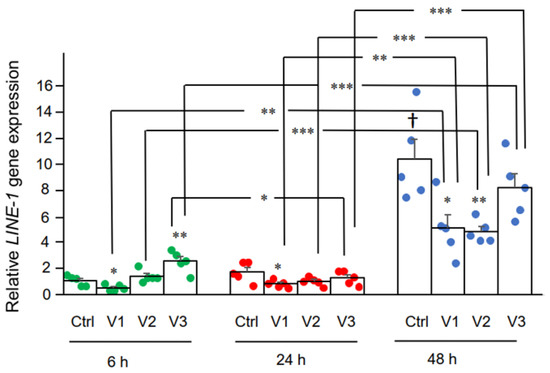
Σχήμα 3. LINE-1 σε κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με BNT162b2. Τα κύτταρα Huh7 υποβλήθηκαν σε επεξεργασία χωρίς (Ctrl) ή με 0,5 (V1), 1 (V2) και 2 μg/mL (V3) BNT162b2 για 6 (πράσινες κουκκίδες), 24 (κόκκινες κουκκίδες) και 48 ώρες (μπλε κουκκίδες) . Το RNA καθαρίστηκε και εκτελέστηκε qPCR χρησιμοποιώντας εκκινητές που στοχεύουν τη LINE-1 . Τα επίπεδα RNA της LINE-1 παρουσιάζονται ως τιμές 2 -ΔΔCT σε σχέση με τα γονίδια οικιακής χρήσης GAPDH και ACTB . Τα αποτελέσματα προέρχονται από πέντε ανεξάρτητα πειράματα ( n = 5). Οι διαφορές μεταξύ των αντίστοιχων ομάδων αναλύθηκαν με τη χρήση t-test Student δύο ουρών . Τα δεδομένα εκφράζονται ως μέσος όρος ± SEM. (* p < 0,05; ** p < 0,01; *** p < 0,001 έναντι του αντίστοιχου ελέγχου σε κάθε χρονικό σημείο, ή όπως υποδεικνύεται, † p < 0,05 έναντι 6 h-Ctrl).
Στη συνέχεια, μελετήσαμε την επίδραση του BNT162b2 στο επίπεδο πρωτεΐνης LINE-1. Η πλήρους μήκους LINE-1 αποτελείται από μια αμετάφραστη περιοχή 5′ (UTR), δύο ανοιχτά πλαίσια ανάγνωσης (ORFs), ORF1 και ORF2 και ένα 3’UTR, από το οποίο το ORF1 είναι μια πρωτεΐνη που δεσμεύει RNA με δραστηριότητα συνοδού. Η δραστηριότητα ρετρομετάθεσης της LINE-1 έχει αποδειχθεί ότι περιλαμβάνει μετατόπιση ORF1 στον πυρήνα [ 35 ]. Κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με ή χωρίς BNT162b2 (0,5, 1,0 και 2,0 μg/mL) για 6 ώρες μονιμοποιήθηκαν και χρωματίστηκαν με αντισώματα που συνδέονται με το LINE-1 ORF1p και ειδικό για το DNA ανιχνευτή Hoechst για οπτικοποίηση του κυτταρικού πυρήνα ( Εικόνα 4 α). Η ποσοτικοποίηση της έντασης χρώσης με ανοσοφθορισμό έδειξε ότι το BNT162b2 αύξησε τα επίπεδα πρωτεΐνης LINE-1 ORF1p τόσο σε ολόκληρη την περιοχή του κυττάρου όσο και στον πυρήνα σε όλες τις συγκεντρώσεις που δοκιμάστηκαν ( Εικόνα 4 b–d).
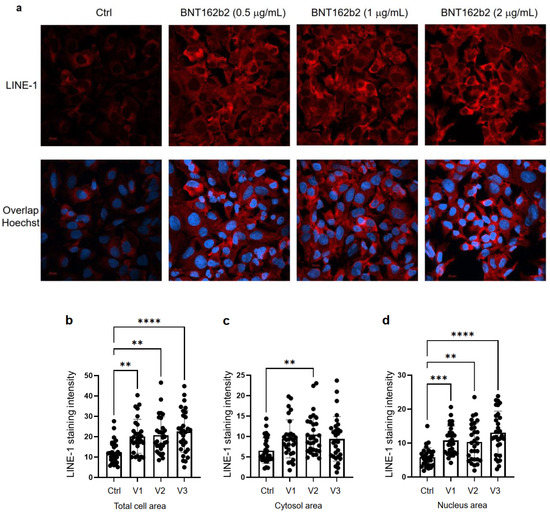
Εικόνα 4. Ανοσοϊστοχημεία κυττάρων Huh7 που υποβλήθηκαν σε επεξεργασία με BNT162b2 σε κατανομή πρωτεΐνης LINE-1. Τα κύτταρα Huh7 υποβλήθηκαν σε επεξεργασία χωρίς (Ctrl) ή με 0,5, 1 και 2 μg/mL BNT162b2 για 6 ώρες. Τα κύτταρα σταθεροποιήθηκαν και χρωματίστηκαν με αντισώματα που συνδέονται με το LINE-1 ORF1p (κόκκινο) και τον ειδικό για DNA ανιχνευτή Hoechst για οπτικοποίηση του κυτταρικού πυρήνα (μπλε). ( α ) Αντιπροσωπευτικές εικόνες της έκφρασης LINE-1 σε κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με ή χωρίς BNT162b2. ( β – δ ) Ποσοτικοποίηση της πρωτεΐνης LINE-1 σε ολόκληρη την κυτταρική περιοχή ( b ), το κυτοσόλιο ( c ) και τον πυρήνα ( d ). Όλα τα δεδομένα αναλύθηκαν χρησιμοποιώντας One-Way ANOVA και δημιουργήθηκαν γραφήματα χρησιμοποιώντας GraphPad Prism V 9.2. Όλα τα δεδομένα παρουσιάζονται ως μέσος όρος ± SD (** p < 0,01, *** p < 0,001, **** p < 0,0001 όπως υποδεικνύεται).
3.3. Ανίχνευση Αντίστροφης Μεταγραφής BNT162b2 DNA σε κύτταρα Huh7
Μια προηγούμενη μελέτη έδειξε ότι η είσοδος της πρωτεΐνης LINE-1 στον πυρήνα σχετίζεται με ρετρομετάθεση [ 35 ]. Στο πείραμα χρώσης με ανοσοφθορισμό που περιγράφηκε παραπάνω, αυξημένα επίπεδα LINE-1 στον πυρήνα παρατηρήθηκαν ήδη στη χαμηλότερη συγκέντρωση BNT162b2 (0,5 μg/mL). Για να εξετάσουμε εάν το BNT162b2 μεταγράφεται αντίστροφα σε DNA όταν η LINE-1 είναι αυξημένη, καθαρίσαμε το γονιδιωματικό DNA από κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με 0,5 μg/mL BNT162b2 για 6, 24 και 48 ώρες. καθαρισμένο DNA υποβλήθηκε σε επεξεργασία με RNase για να απομακρυνθεί το RNA και υποβλήθηκε σε PCR χρησιμοποιώντας εκκινητές που στοχεύουν το BNT162b2, όπως απεικονίζεται στο Σχήμα 1 . Τα ενισχυμένα θραύσματα DΝΑ στη συνέχεια οπτικοποιήθηκαν με ηλεκτροφόρηση και καθαρίστηκαν με πήκτωμα ( Εικόνα 5 ). Τα αμπλικόνια DNA BNT162b2 ανιχνεύθηκαν και στα τρία χρονικά σημεία (6, 24 και 48 ώρες). Η αλληλουχία Sanger επιβεβαίωσε ότι τα αμπλικόνια DNA ήταν πανομοιότυπα με την αλληλουχία BNT162b2 που πλαισιώνεται από τους εκκινητές ( Πίνακας 2 ). Για να διασφαλίσουμε ότι τα αμπλικόνια DNA προέρχονταν από DNA αλλά όχι από BNT162b2 RNA, πραγματοποιήσαμε επίσης PCR σε RNA καθαρισμένο από κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με 0,5 μg/mL BNT162b2 για 6 ώρες, με ή χωρίς θεραπεία με RNase (Ctrl 5 και 6 in Σχήμα 5 ), και δεν ανιχνεύθηκε αμπλικόνιο στα δείγματα RNA που υποβλήθηκαν σε PCR.
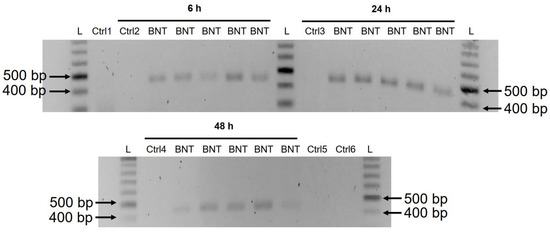
Εικόνα 5. Ανίχνευση αμπλικονίων DNA του BNT162b2 σε κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με BNT162b2. Τα κύτταρα Huh7 υποβλήθηκαν σε επεξεργασία χωρίς (Ctrl) ή με 0,5 μg/mL BNT162b2 για 6, 24 και 48 ώρες. Το γονιδιωματικό DNA καθαρίστηκε και υποβλήθηκε σε πέψη με 100 μg/mL RNase. Η PCR εκτελέστηκε σε όλα τα δείγματα με εκκινητές που στοχεύουν το BNT162b2, όπως φαίνεται στο Σχήμα 1 και στον Πίνακα 1 . Τα αμπλικόνια DNA (444 bps) εμφανίστηκαν σε πήκτωμα αγαρόζης. BNT: BNT162b2; L: Κλίμακα DNA; Ctrl1: καλλιεργημένα κύτταρα Huh7. Ctrl2: Κύτταρα Huh7 χωρίς επεξεργασία BNT162b2 που συλλέχθηκαν στις 6 ώρες. Ctrl3: Κύτταρα Huh7 χωρίς επεξεργασία BNT162b2 που συλλέχθηκαν στις 24 ώρες. Ctrl4: Κύτταρα Huh7 χωρίς επεξεργασία BNT162b2 που συλλέχθηκαν στις 48 ώρες. Ctrl5: RNA από κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με 0,5 μg/mL BNT162b2 για 6 ώρες. Ctrl6: RNA από κύτταρα Huh7 που υποβλήθηκαν σε επεξεργασία με 0,5 μg/mL BNT162b2 για 6 ώρες, χωνευμένο με RNase.
Πίνακας 2. Αποτέλεσμα αλληλουχίας Sanger του ενισχυτικού BNT162b2.

4. Συζήτηση
Σε αυτή τη μελέτη παρουσιάζουμε στοιχεία ότι το εμβόλιο mRNA του COVID-19 BNT162b2 μπορεί να εισέλθει στην κυτταρική σειρά ανθρώπινου ήπατος Huh7 in vitro. Το mRNA του BNT162b2 μεταγράφεται αντίστροφα ενδοκυτταρικά στο DNA τόσο γρήγορα όσο 6 ώρες μετά την έκθεση στο BNT162b2. Ένας πιθανός μηχανισμός για την αντίστροφη μεταγραφή είναι μέσω της ενδογενούς ανάστροφης μεταγραφάσης LINE-1, και η κατανομή πρωτεΐνης πυρήνα της LINE-1 αυξάνεται από το BNT162b2.
Η ενδοκυτταρική συσσώρευση LNP στα ηπατοκύτταρα έχει αποδειχθεί in vivo [ 36 ]. Μια προκλινική μελέτη για το BNT162b2 έδειξε ότι το BNT162b2 εισέρχεται στα κύτταρα HEK293T της ανθρώπινης κυτταρικής σειράς και οδηγεί σε ισχυρή έκφραση του αντιγόνου BNT162b2 [ 37 ]. Επομένως, σε αυτή τη μελέτη, διερευνήσαμε αρχικά την είσοδο του BNT162b2 στα κύτταρα Huh7 της ανθρώπινης κυτταρικής σειράς ήπατος. Η επιλογή των συγκεντρώσεων BNT162b2 που χρησιμοποιούνται σε αυτή τη μελέτη δικαιολογεί εξήγηση. Το BNT162b2 χορηγείται ως μια σειρά δύο δόσεων με διαφορά τριών εβδομάδων και κάθε δόση περιέχει 30 μg BNT162b2 σε όγκο 0,3 mL, γεγονός που καθιστά την τοπική συγκέντρωση στο σημείο της ένεσης στο υψηλότερο 100 μg/mL [ 31 ]. Μια προηγούμενη μελέτη για τα εμβόλια mRNA κατά των ιών γρίπης H10N8 και H7N9 χρησιμοποιώντας ένα παρόμοιο σύστημα χορήγησης LNP έδειξε ότι το εμβόλιο mRNA μπορεί να κατανεμηθεί μάλλον μη ειδικά σε πολλά όργανα όπως το ήπαρ, ο σπλήνας, η καρδιά, τα νεφρά, οι πνεύμονες και ο εγκέφαλος και η συγκέντρωση στο συκώτι είναι περίπου 100 φορές χαμηλότερο από αυτό του σημείου της ενδομυϊκής ένεσης [ 38 ]. Στην έκθεση αξιολόγησης του BNT162b2 που παρασχέθηκε στον EMA από την Pfizer, οι μελέτες φαρμακοκινητικής κατανομής σε αρουραίους έδειξαν ότι ένα σχετικά μεγάλο ποσοστό (έως 18%) της συνολικής δόσης κατανέμεται στο ήπαρ [ 26 ]. Ως εκ τούτου, επιλέξαμε να χρησιμοποιήσουμε 0,5, 1 και 2 μg/mL εμβολίου στα πειράματά μας στα ηπατικά κύτταρα. Ωστόσο, η επίδραση ενός ευρύτερου εύρους χαμηλότερων και υψηλότερων συγκεντρώσεων BNT162b2 θα πρέπει επίσης να επαληθευτεί σε μελλοντικές μελέτες.
Στην τρέχουσα μελέτη, χρησιμοποιήσαμε μια ανθρώπινη κυτταρική σειρά ήπατος για in vitro έρευνα. Αξίζει να διερευνηθεί εάν τα ηπατικά κύτταρα παρουσιάζουν επίσης την πρωτεΐνη ακίδας SARS-CoV-2 που προέρχεται από το εμβόλιο, η οποία θα μπορούσε δυνητικά να καταστήσει τα ηπατικά κύτταρα στόχους για κυτταροτοξικά Τ κύτταρα που αντιδρούν με πρωτεΐνες ακίδας. Έχουν υπάρξει αναφορές περιστατικών σε άτομα που ανέπτυξαν αυτοάνοση ηπατίτιδα [ 39 ] μετά τον εμβολιασμό BNT162b2. Για την καλύτερη κατανόηση των πιθανών επιδράσεων του BNT162b2 στην ηπατική λειτουργία, είναι επιθυμητά μοντέλα in vivo για μελλοντικές μελέτες.
Στην έκθεση τοξικότητας BNT162b2, δεν έχουν παρασχεθεί μελέτες γονοτοξικότητας ή καρκινογένεσης [ 26 ]. Η μελέτη μας δείχνει ότι το BNT162b2 μπορεί να μεταγραφεί αντίστροφα σε DNA στην ηπατική κυτταρική σειρά Huh7 και αυτό μπορεί να προκαλέσει ανησυχία εάν το DNA που προέρχεται από BNT162b2 μπορεί να ενσωματωθεί στο γονιδίωμα του ξενιστή και να επηρεάσει την ακεραιότητα του γονιδιωματικού DNA, το οποίο μπορεί να μεσολαβήσει δυνητικά γονιδιοτοξικά παρενέργειες. Σε αυτό το στάδιο, δεν γνωρίζουμε εάν το DNA που μεταγράφεται αντίστροφα από το BNT162b2 είναι ενσωματωμένο στο γονιδίωμα του κυττάρου. Απαιτούνται περαιτέρω μελέτες για να καταδειχθεί η επίδραση του BNT162b2 στη γονιδιωματική ακεραιότητα, συμπεριλαμβανομένης της αλληλουχίας ολόκληρου του γονιδιώματος των κυττάρων που εκτέθηκαν στο BNT162b2, καθώς και των ιστών από ανθρώπινα υποκείμενα που έλαβαν εμβολιασμό BNT162b2.
Το ανθρώπινο αυτόνομο ρετροτρανσποζόνιο LINE-1 είναι μια κυτταρική ενδογενής αντίστροφη τρανσκριπτάση και το μόνο εναπομείναν ενεργό τρανσποζόνιο στον άνθρωπο, ικανό να ρετρομεταθέτει τον εαυτό του και άλλα μη αυτόνομα στοιχεία [ 40 , 41 ], και ~17% του ανθρώπινου γονιδιώματος αποτελείται από αλληλουχίες LINE-1 [ 42 ]. Τα Alu , σύντομα, διάσπαρτα νουκλεοτιδικά στοιχεία (SINEs), μεταβλητός αριθμός διαδοχικών επαναλήψεων (VNTR), καθώς και κυτταρικά επεξεργασμένα από mRNA ψευδογονίδια, μεταφέρονται εκ των υστέρων από τις πρωτεΐνες ρετρομεταφοράς LINE-1 που λειτουργούν σε trans [ 43 , 44 ]. Μια πρόσφατη μελέτη έδειξε ότι η ενδογενής LINE-1 μεσολαβεί στην αντίστροφη μεταγραφή και ενσωμάτωση των αλληλουχιών SARS-CoV-2 στα γονιδιώματα των μολυσμένων ανθρώπινων κυττάρων [ 25 ]. Επιπλέον, η έκφραση της ενδογενούς LINE-1 συχνά αυξάνεται με ιογενή λοίμωξη, συμπεριλαμβανομένης της μόλυνσης από SARS-CoV-2 [ 45 , 46 , 47 ]. Προηγούμενες μελέτες έδειξαν ότι η δραστηριότητα ρετρομετάθεσης LINE-1 ρυθμίζεται από το μεταβολισμό του RNA [ 48 , 49 ], την απόκριση βλάβης στο DNA [ 50 ] και την αυτοφαγία [ 51 ]. Η αποτελεσματική ρετρομεταφορά της LINE-1 συχνά σχετίζεται με τη διάσπαση του κυτταρικού κύκλου και του πυρηνικού φακέλου κατά τη διάρκεια της μίτωσης. 52 , 53 ], καθώς και εξωγενείς ρετροϊούς [ 54 , 55 ], που προάγει την είσοδο της LINE-1 στον πυρήνα. Στη μελέτη μας, παρατηρήσαμε αυξημένη κατανομή LINE-1 ORF1p όπως προσδιορίστηκε από την ανοσοϊστοχημεία στον πυρήνα από το BNT162b2 σε όλες τις συγκεντρώσεις που δοκιμάστηκαν (0,5, 1 και 2 μg/mL), ενώ LINE-1 ανιχνεύθηκε αυξημένη έκφραση γονιδίου συγκέντρωσης (2 μg/mL). Αξίζει να σημειωθεί ότι η γονιδιακή μεταγραφή ρυθμίζεται από τροποποιήσεις χρωματίνης, ρύθμιση παραγόντων μεταγραφής και ρυθμό αποικοδόμησης RNA, ενώ η μεταφραστική ρύθμιση της πρωτεΐνης περιλαμβάνει στρατολόγηση ριβοσώματος στο κωδικόνιο έναρξης, ρύθμιση επιμήκυνσης πεπτιδίου, τερματισμό της πρωτεϊνικής σύνθεσης ή βιογένεση ριβοσώματος . Αυτές οι δύο διαδικασίες ελέγχονται από διαφορετικούς μηχανισμούς και επομένως μπορεί να μην εμφανίζουν πάντα τα ίδια μοτίβα αλλαγής ως απάντηση σε εξωτερικές προκλήσεις. Η ακριβής ρύθμιση της δραστηριότητας LINE-1 ως απόκριση στο BNT162b2 αξίζει περαιτέρω μελέτη.
Το κυτταρικό μοντέλο που χρησιμοποιήσαμε σε αυτή τη μελέτη είναι μια κυτταρική σειρά καρκινώματος, (σ.γ.:τα οποία προσφέρονται για καλλιέργεια επειδή διαιρούνται αενάως) με ενεργό αντιγραφή DNA που διαφέρει από τα μη διαιρούμενα σωματικά κύτταρα. Έχει επίσης αποδειχθεί ότι τα κύτταρα Huh7 εμφανίζουν σημαντική διαφορετική έκφραση γονιδίων και πρωτεϊνών συμπεριλαμβανομένων των προς τα πάνω ρυθμιζόμενων πρωτεϊνών που εμπλέκονται στο μεταβολισμό του RNA [ 56 ]. Ωστόσο, ο κυτταρικός πολλαπλασιασμός είναι επίσης ενεργός σε αρκετούς ανθρώπινους ιστούς, όπως ο μυελός των οστών ή οι βασικές στοιβάδες των επιθηλίων, καθώς και κατά τη διάρκεια της εμβρυογένεσης, και επομένως είναι απαραίτητο να εξεταστεί η επίδραση του BNT162b2 στη γονιδιωματική ακεραιότητα υπό τέτοιες συνθήκες. Επιπλέον, έχει επίσης αναφερθεί αποτελεσματική ρετρομετάθεση της LINE-1 σε μη διαιρούμενα και τερματικά διαφοροποιημένα κύτταρα, όπως οι ανθρώπινοι νευρώνες [ 57 , 58 ].
Η έκθεση αξιολόγησης της Pfizer στην EMA έδειξε επίσης ότι το BNT162b2 κατανέμεται στη σπλήνα (<1,1%), στα επινεφρίδια (<0,1%), καθώς και χαμηλή και μετρήσιμη ραδιενέργεια υπήρχε στις ωοθήκες και τους όρχεις (<0,1%) [ 26 ]. Επιπλέον, δεν υπάρχουν διαθέσιμα δεδομένα σχετικά με τη μεταφορά του BNT162b2 από τον πλακούντα από την έκθεση αξιολόγησης EMA της Pfizer. Τα αποτελέσματά μας έδειξαν ότι το mRNA BNT162b2 εισέρχεται εύκολα στα κύτταρα Huh7 σε συγκέντρωση (0,5 μg/mL) που αντιστοιχεί στο 0,5% της τοπικής συγκέντρωσης στο σημείο της ένεσης, επάγει αλλαγές στο γονίδιο LINE-1 και την έκφραση πρωτεΐνης και εντός 6 ωρών αντίστροφη μεταγραφή του BNT162b2 μπορεί να ανιχνευθεί. Είναι επομένως σημαντικό να διερευνηθεί περαιτέρω η επίδραση του BNT162b2 σε άλλους κυτταρικούς τύπους και ιστούς τόσο in vitro όσο και in vivo.
5. Συμπεράσματα
Η μελέτη μας είναι η πρώτη in vitro μελέτη σχετικά με την επίδραση του εμβολίου mRNA του COVID-19 BNT162b2 στην κυτταρική σειρά ανθρώπινου ήπατος. Παρουσιάζουμε στοιχεία σχετικά με τη γρήγορη είσοδο του BNT162b2 στα κύτταρα και την επακόλουθη ενδοκυτταρική αντίστροφη μεταγραφή του BNT162b2 mRNA στο DNA.
Συμπληρωματικά Υλικά
Μπορείτε να λάβετε τις ακόλουθες υποστηρικτικές πληροφορίες στη διεύθυνση: https://www.mdpi.com/article/10.3390/cimb44030073/s1 .
Συνεισφορές Συγγραφέων
Οι MA, FOF, DY, MB και CL πραγματοποίησαν πειράματα in vitro. Οι MA και FOF πραγματοποίησαν ανάλυση δεδομένων. Η MR και η YDM συνέβαλαν στην υλοποίηση της έρευνας, σχεδίασαν και επέβλεψαν τη μελέτη. Το YDM έγραψε την εργασία με τη συμβολή όλων των συγγραφέων. Όλοι οι συγγραφείς έχουν διαβάσει και έχουν συμφωνήσει με τη δημοσιευμένη έκδοση του χειρογράφου.
Χρηματοδότηση
Αυτή η μελέτη υποστηρίχθηκε από το Σουηδικό Ερευνητικό Συμβούλιο, Strategic Research Area Exodiab, Dnr 2009-1039, το Σουηδικό Κυβερνητικό Ταμείο για την Κλινική Έρευνα (ALF) και το ίδρυμα του Πανεπιστημιακού Νοσοκομείου Skåne.
Δήλωση του Συμβουλίου Θεσμικής Αναθεώρησης
Δεν εφαρμόζεται.
Δήλωση ενημερωμένης συναίνεσης
Δεν εφαρμόζεται.
Δήλωση διαθεσιμότητας δεδομένων
Όλα τα δεδομένα που υποστηρίζουν τα ευρήματα αυτής της μελέτης είναι διαθέσιμα εντός του άρθρου και των υποστηρικτικών πληροφοριών .
Ευχαριστίες
Οι συγγραφείς ευχαριστούν τους Sven Haidl, Maria Josephson, Enming Zhang, Jia-Yi Li, Caroline Haikal και Pradeep Bompada για την υποστήριξή τους σε αυτή τη μελέτη.
Συγκρούσεις συμφερόντων
Οι συγγραφείς δηλώνουν ότι δεν υπάρχει σύγκρουση συμφερόντων.
Intracellular Reverse Transcription of Pfizer BioNTech COVID-19 mRNA Vaccine BNT162b2 In Vitro in Human Liver Cell Line
1
Department of Clinical Sciences, Lund University, 20502 Malmö, Sweden
2
Infection Medicine, Department of Clinical Sciences, Lund University, 22362 Lund, Sweden
*
Author to whom correspondence should be addressed.
Academic Editor: Stephen Malnick
Curr. Issues Mol. Biol. 2022, 44(3), 1115-1126; https://doi.org/10.3390/cimb44030073
Received: 18 January 2022 / Revised: 19 February 2022 / Accepted: 23 February 2022 / Published: 25 February 2022
(This article belongs to the Topic Clinical, Translational and Basic Research on Liver Diseases)
Abstract
Preclinical studies of COVID-19 mRNA vaccine BNT162b2, developed by Pfizer and BioNTech, showed reversible hepatic effects in animals that received the BNT162b2 injection. Furthermore, a recent study showed that SARS-CoV-2 RNA can be reverse-transcribed and integrated into the genome of human cells. In this study, we investigated the effect of BNT162b2 on the human liver cell line Huh7 in vitro. Huh7 cells were exposed to BNT162b2, and quantitative PCR was performed on RNA extracted from the cells. We detected high levels of BNT162b2 in Huh7 cells and changes in gene expression of long interspersed nuclear element-1 (LINE-1), which is an endogenous reverse transcriptase. Immunohistochemistry using antibody binding to LINE-1 open reading frame-1 RNA-binding protein (ORFp1) on Huh7 cells treated with BNT162b2 indicated increased nucleus distribution of LINE-1. PCR on genomic DNA of Huh7 cells exposed to BNT162b2 amplified the DNA sequence unique to BNT162b2. Our results indicate a fast up-take of BNT162b2 into human liver cell line Huh7, leading to changes in LINE-1 expression and distribution. We also show that BNT162b2 mRNA is reverse transcribed intracellularly into DNA in as fast as 6 h upon BNT162b2 exposure.
1. Introduction
Coronavirus disease 2019 (COVID-19) caused by severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) was announced by the World Health Organization (WHO) as a global pandemic on 11 March 2020, and it emerged as a devasting health crisis. As of February 2022, COVID-19 has led to over 430 million reported infection cases and 5.9 million deaths worldwide [1]. Effective and safe vaccines are urgently needed to reduce the morbidity and mortality rates associated with COVID-19.
Several vaccines for COVID-19 have been developed, with particular focus on mRNA vaccines (by Pfizer-BioNTech and Moderna), replication-defective recombinant adenoviral vector vaccines (by Janssen-Johnson and Johnson, Astra-Zeneca, Sputnik-V, and CanSino), and inactivated vaccines (by Sinopharm, Bharat Biotech and Sinovac). The mRNA vaccine has the advantages of being flexible and efficient in immunogen design and manufacturing, and currently, numerous vaccine candidates are in various stages of development and application. Specifically, COVID-19 mRNA vaccine BNT162b2 developed by Pfizer and BioNTech has been evaluated in successful clinical trials [2,3,4] and administered in national COVID-19 vaccination campaigns in different regions around the world [5,6,7,8].
BNT162b2 is a lipid nanoparticle (LNP)–encapsulated, nucleoside-modified RNA vaccine (modRNA) and encodes the full-length of SARS-CoV-2 spike (S) protein, modified by two proline mutations to ensure antigenically optimal pre-fusion conformation, which mimics the intact virus to elicit virus-neutralizing antibodies [3]. Consistent with randomized clinical trials, BNT162b2 showed high efficiency in a wide range of COVID-19-related outcomes in a real-world setting [5]. Nevertheless, many challenges remain, including monitoring for long-term safety and efficacy of the vaccine. This warrants further evaluation and investigations. The safety profile of BNT162b2 is currently only available from short-term clinical studies. Less common adverse effects of BNT162b2 have been reported, including pericarditis, arrhythmia, deep-vein thrombosis, pulmonary embolism, myocardial infarction, intracranial hemorrhage, and thrombocytopenia [4,9,10,11,12,13,14,15,16,17,18,19,20]. There are also studies that report adverse effects observed in other types of vaccines [21,22,23,24]. To better understand mechanisms underlying vaccine-related adverse effects, clinical investigations as well as cellular and molecular analyses are needed.
A recent study showed that SARS-CoV-2 RNAs can be reverse-transcribed and integrated into the genome of human cells [25]. This gives rise to the question of if this may also occur with BNT162b2, which encodes partial SARS-CoV-2 RNA. In pharmacokinetics data provided by Pfizer to European Medicines Agency (EMA), BNT162b2 biodistribution was studied in mice and rats by intra-muscular injection with radiolabeled LNP and luciferase modRNA. Radioactivity was detected in most tissues from the first time point (0.25 h), and results showed that the injection site and the liver were the major sites of distribution, with maximum concentrations observed at 8–48 h post-dose [26]. Furthermore, in animals that received the BNT162b2 injection, reversible hepatic effects were observed, including enlarged liver, vacuolation, increased gamma glutamyl transferase (γGT) levels, and increased levels of aspartate transaminase (AST) and alkaline phosphatase (ALP) [26]. Transient hepatic effects induced by LNP delivery systems have been reported previously [27,28,29,30], nevertheless, it has also been shown that the empty LNP without modRNA alone does not introduce any significant liver injury [27]. Therefore, in this study, we aim to examine the effect of BNT162b2 on a human liver cell line in vitro and investigate if BNT162b2 can be reverse transcribed into DNA through endogenous mechanisms.
2. Materials and Methods
2.1. Cell Culture
Huh7 cells (JCRB Cell Bank, Osaka, Japan) were cultured in 37 °C at 5% CO2 with DMEM medium (HyClone, HYCLSH30243.01) supplemented with 10% (v/v) fetal bovine serum (Sigma-Aldrich, F7524-500ML, Burlington, MA, USA) and 1% (v/v) Penicillin-Streptomycin (HyClone, SV30010, Logan, UT, USA). For BNT162b2 treatment, Huh7 cells were seeded with a density of 200,000 cells/well in 24-well plates. BNT162b2 mRNA vaccine (Pfizer BioNTech, New York, NY, USA) was diluted with sterile 0.9% sodium chloride injection, USP into a final concentration of 100 μg/mL as described in the manufacturer’s guideline [31]. BNT162b2 suspension was then added in cell culture media to reach final concentrations of 0.5, 1.0, or 2.0 μg/mL. Huh7 cells were incubated with or without BNT162b2 for 6, 24, and 48 h. Cells were washed thoroughly with PBS and harvested by trypsinization and stored in −80 °C until further use.
2.2. REAL-TIME RT-QPCR
RNA from the cells was extracted with RNeasy Plus Mini Kit (Qiagen, 74134, Hilden, Germany) following the manufacturer’s protocol. RT-PCR was performed using RevertAid First Strand cDNA Synthesis kit (Thermo Fisher Scientific, K1622, Waltham, MA, USA) following the manufacturers protocol. Real-time qPCR was performed using Maxima SYBR Green/ROX qPCR Master Mix (Thermo Fisher Scientific, K0222, Waltham, MA, USA) with primers for BNT162b2, LINE-1 and housekeeping genes ACTB and GAPDH (Table 1).
Table 1. Primer sequences of RT-qPCR and PCR.

2.3. Immunofluorescence Staining and Confocal Imaging
Huh7 cells were cultured in eight-chamber slides (LAB-TEK, 154534, Santa Cruz, CA, USA) with a density of 40,000 cells/well, with or without BNT162b2 (0.5, 1 or 2 µg/mL) for 6 h. Immunohistochemistry was performed using primary antibody anti-LINE-1 ORF1p mouse monoclonal antibody (Merck, 3574308, Kenilworth, NJ, USA), secondary antibody Cy3 Donkey anti-mouse (Jackson ImmunoResearch, West Grove, PA, USA), and Hoechst (Life technologies, 34850, Carlsbad, CA, USA), following the protocol from Thermo Fisher (Waltham, MA, USA). Two images per condition were taken using a Zeiss LSM 800 and a 63X oil immersion objective, and the staining intensity was quantified on the individual whole cell area and the nucleus area on 15 cells per image by ImageJ 1.53c. LINE-1 staining intensity for the cytosol was calculated by subtracting the intensity of the nucleus from that of the whole cell. All images of the cells were assigned a random number to prevent bias. To mark the nuclei (determined by the Hoechst staining) and the whole cells (determined by the borders of the LINE-1 fluorescence), the Freehand selection tool was used. These areas were then measured, and the mean intensity was used to compare the groups.
2.4. Genomic DNA Purification, PCR Amplification, Agarose Gel Purification, and Sanger Sequencing
Genomic DNA was extracted from cell pellets with PBND buffer (10 mM Tris-HCl pH 8.3, 50 mM KCl, 2.5 mM MgCl2, 0.45% NP-40, 0.45% Tween-20) according to protocol described previously [32]. To remove residual RNA from the DNA preparation, RNase (100 µg/mL, Qiagen, Hilden, Germany) was added to the DNA preparation and incubated at 37 °C for 3 h, followed by 5 min at 95 °C. PCR was then performed using primers targeting BNT162b2 (sequences are shown in Table 1), with the following program: 5 min at 95 °C, 35 cycles of 95 °C for 30 s, 58 °C for 30 s, and 72 °C for 1 min; finally, 72 °C for 5 min and 12 °C for 5 min. PCR products were run on 1.4% (w/v) agarose gel. Bands corresponding to the amplicons of the expected size (444 bps) were cut out and DNA was extracted using QIAquick PCR Purification Kit (Qiagen, 28104, Hilden, Germany), following the manufacturer’s instructions. The sequence of the DNA amplicon was verified by Sanger sequencing (Eurofins Genomics, Ebersberg, Germany).
Statistics
Statistical comparisons were performed using two-tailed Student’s t-test and ANOVA. Data are expressed as the mean ± SEM or ± SD. Differences with p < 0.05 are considered significant.
2.5. Ethical Statements
The Huh7 cell line was obtained from Japanese Collection of Research Bioresources (JCRB) Cell Bank.
3. Results
3.1. BNT162b2 Enters Human Liver Cell Line Huh7 Cells at High Efficiency
To determine if BNT162b2 enters human liver cells, we exposed human liver cell line Huh7 to BNT162b2. In a previous study on the uptake kinetics of LNP delivery in Huh7 cells, the maximum biological efficacy of LNP was observed between 4–7 h [33]. Therefore, in our study, Huh7 cells were cultured with or without increasing concentrations of BNT162b2 (0.5, 1.0 and 2.0 µg/mL) for 6, 24, and 48 h. RNA was extracted from cells and a real-time quantitative reverse transcription polymerase chain reaction (RT-qPCR) was performed using primers targeting the BNT162b2 sequence, as illustrated in Figure 1. The full sequence of BNT162b2 is publicly available [34] and contains a two-nucleotides cap; 5′- untranslated region (UTR) that incorporates the 5′ -UTR of a human α-globin gene; the full-length of SARS-CoV-2 S protein with two proline mutations; 3′-UTR that incorporates the human mitochondrial 12S rRNA (mtRNR1) segment and human AES/TLE5 gene segment with two C→U mutations; poly(A) tail. Detailed analysis of the S protein sequence in BNT162b2 revealed 124 sequences that are 100% identical to human genomic sequences and three sequences with only one nucleotide (nt) mismatch in 19–26 nts (Table S1, see Supplementary Materials). To detect BNT162b2 RNA level, we designed primers with forward primer located in SARS-CoV-2 S protein regions and reverse primer in 3′-UTR, which allows detection of PCR amplicon unique to BNT162b2 without unspecific binding of the primers to human genomic regions.

Figure 1. PCR primer set used to detect mRNA level and reverse-transcription of BNT162b2. Illustration of BNT162b2 was adapted from previously described literature [34].
RT-qPCR results showed that Huh7 cells treated with BNT162b2 had high levels of BNT162b2 mRNA relative to housekeeping genes at 6, 24, and 48 h (Figure 2, presented in logged 2−ΔΔCT due to exceptionally high levels). The three BNT162b2 concentrations led to similar intracellular BNT162b2 mRNA levels at the different time points, except that the significant difference between 1.0 and 2.0 µg/mL was observed at 48 h. BNT162b2 mRNA levels were significantly decreased at 24 h compared to 6 h, but increased again at 48 h.

Figure 2. BNT162b2 mRNA levels in Huh7 cells treated with BNT162b2. Huh7 cells were treated without (Ctrl) or with 0.5 (V1), 1 (V2), and 2 µg/mL (V3) of BNT162b2 for 6 (green dots), 24 (orange dots), and 48 h (blue dots). RNA was purified and qPCR was performed using primers targeting BNT162b2. RNA levels of BNT162b2 are presented as logged 2−ΔΔCT values relative to house-keeping genes GAPDH and ACTB. Results are from five independent experiments (n = 5). Differences between respective groups were analyzed using two-tailed Student’s t-test. Data are expressed as the mean ± SEM. (* p < 0.05; ** p < 0.01; *** p < 0.001 vs. respective control at each time point, or as indicated).
3.2. Effect of BNT162b2 on Human Endogenous Reverse Transcriptase Long Interspersed Nuclear Element-1 (LINE-1)
Here we examined the effect of BNT162b2 on LINE-1 gene expression. RT-qPCR was performed on RNA purified from Huh7 cells treated with BNT162b2 (0, 0.5, 1.0, and 2.0 µg/mL) for 6, 24, and 48 h, using primers targeting LINE-1. Significantly increased LINE-1 expression compared to control was observed at 6 h by 2.0 µg/mL BNT162b2, while lower BNT162b2 concentrations decreased LINE-1 expression at all time points (Figure 3).

Figure 3. LINE-1 mRNA levels in Huh7 cells treated with BNT162b2. Huh7 cells were treated without (Ctrl) or with 0.5 (V1), 1 (V2), and 2 µg/mL (V3) of BNT162b2 for 6 (green dots), 24 (red dots), and 48 h (blue dots). RNA was purified and qPCR was performed using primers targeting LINE-1. RNA levels of LINE-1 are presented as 2−ΔΔCT values relative to house-keeping genes GAPDH and ACTB. Results are from five independent experiments (n = 5). Differences between respective groups were analyzed using two-tailed Student’s t-test. Data are expressed as the mean ± SEM. (* p < 0.05; ** p < 0.01; *** p < 0.001 vs. respective control at each time point, or as indicated; † p < 0.05 vs. 6 h-Ctrl).
Next, we studied the effect of BNT162b2 on LINE-1 protein level. The full-length LINE-1 consists of a 5′ untranslated region (UTR), two open reading frames (ORFs), ORF1 and ORF2, and a 3′UTR, of which ORF1 is an RNA binding protein with chaperone activity. The retrotransposition activity of LINE-1 has been demonstrated to involve ORF1 translocation to the nucleus [35]. Huh7 cells treated with or without BNT162b2 (0.5, 1.0 and 2.0 µg/mL) for 6 h were fixed and stained with antibodies binding to LINE-1 ORF1p, and DNA-specific probe Hoechst for visualization of cell nucleus (Figure 4a). Quantification of immunofluorescence staining intensity showed that BNT162b2 increased LINE-1 ORF1p protein levels in both the whole cell area and nucleus at all concentrations tested (Figure 4b–d).

Figure 4. Immunohistochemistry of Huh7 cells treated with BNT162b2 on LINE-1 protein distribution. Huh7 cells were treated without (Ctrl) or with 0.5, 1, and 2 µg/mL of BNT162b2 for 6 h. Cells were fixed and stained with antibodies binding to LINE-1 ORF1p (red) and DNA-specific probe Hoechst for visualization of cell nucleus (blue). (a) Representative images of LINE-1 expression in Huh7 cells treated with or without BNT162b2. (b–d) Quantification of LINE-1 protein in whole cell area (b), cytosol (c), and nucleus (d). All data were analyzed using One-Way ANOVA, and graphs were created using GraphPad Prism V 9.2. All data is presented as mean ± SD (** p < 0.01; *** p < 0.001; **** p < 0.0001 as indicated).
3.3. Detection of Reverse Transcribed BNT162b2 DNA in Huh7 Cells
A previous study has shown that entry of LINE-1 protein into the nucleus is associated with retrotransposition [35]. In the immunofluorescence staining experiment described above, increased levels of LINE-1 in the nucleus were observed already at the lowest concentration of BNT162b2 (0.5 µg/mL). To examine if BNT162b2 is reversely transcribed into DNA when LINE-1 is elevated, we purified genomic DNA from Huh7 cells treated with 0.5 µg/mL of BNT162b2 for 6, 24, and 48 h. Purified DNA was treated with RNase to remove RNA and subjected to PCR using primers targeting BNT162b2, as illustrated in Figure 1. Amplified DNA fragments were then visualized by electrophoresis and gel-purified (Figure 5). BNT162b2 DNA amplicons were detected in all three time points (6, 24, and 48 h). Sanger sequencing confirmed that the DNA amplicons were identical to the BNT162b2 sequence flanked by the primers (Table 2). To ensure that the DNA amplicons were derived from DNA but not BNT162b2 RNA, we also performed PCR on RNA purified from Huh7 cells treated with 0.5 µg/mL BNT162b2 for 6 h, with or without RNase treatment (Ctrl 5 and 6 in Figure 5), and no amplicon was detected in the RNA samples subjected to PCR.

Figure 5. Detection of DNA amplicons of BNT162b2 in Huh7 cells treated with BNT162b2. Huh7 cells were treated without (Ctrl) or with 0.5 µg/mL of BNT162b2 for 6, 24, and 48 h. Genomic DNA was purified and digested with 100 µg/mL RNase. PCR was run on all samples with primers targeting BNT162b2, as shown in Figure 1 and Table 1. DNA amplicons (444 bps) were visualized on agarose gel. BNT: BNT162b2; L: DNA ladder; Ctrl1: cultured Huh7 cells; Ctrl2: Huh7 cells without BNT162b2 treatment collected at 6 h; Ctrl3: Huh7 cells without BNT162b2 treatment collected at 24 h; Ctrl4: Huh7 cells without BNT162b2 treatment collected at 48 h; Ctrl5: RNA from Huh7 cells treated with 0.5 µg/mL of BNT162b2 for 6 h; Ctrl6: RNA from Huh7 cells treated with 0.5 µg/mL of BNT162b2 for 6 h, digested with RNase.
Table 2. Sanger sequencing result of the BNT162b2 amplicon.

4. Discussion
In this study we present evidence that COVID-19 mRNA vaccine BNT162b2 is able to enter the human liver cell line Huh7 in vitro. BNT162b2 mRNA is reverse transcribed intracellularly into DNA as fast as 6 h after BNT162b2 exposure. A possible mechanism for reverse transcription is through endogenous reverse transcriptase LINE-1, and the nucleus protein distribution of LINE-1 is elevated by BNT162b2.
Intracellular accumulation of LNP in hepatocytes has been demonstrated in vivo [36]. A preclinical study on BNT162b2 showed that BNT162b2 enters the human cell line HEK293T cells and leads to robust expression of BNT162b2 antigen [37]. Therefore, in this study, we first investigated the entry of BNT162b2 in the human liver cell line Huh7 cells. The choice of BNT162b2 concentrations used in this study warrants explanation. BNT162b2 is administered as a series of two doses three weeks apart, and each dose contains 30 µg of BNT162b2 in a volume of 0.3 mL, which makes the local concentration at the injection site at the highest 100 µg/mL [31]. A previous study on mRNA vaccines against H10N8 and H7N9 influenza viruses using a similar LNP delivery system showed that the mRNA vaccine can distribute rather nonspecifically to several organs such as liver, spleen, heart, kidney, lung, and brain, and the concentration in the liver is roughly 100 times lower than that of the intra-muscular injection site [38]. In the assessment report on BNT162b2 provided to EMA by Pfizer, the pharmacokinetic distribution studies in rats demonstrated that a relatively large proportion (up to 18%) of the total dose distributes to the liver [26]. We therefore chose to use 0.5, 1, and 2 μg/mL of vaccine in our experiments on the liver cells. However, the effect of a broader range of lower and higher concentrations of BNT162b2 should also be verified in future studies.
In the current study, we employed a human liver cell line for in vitro investigation. It is worth investigating if the liver cells also present the vaccine-derived SARS-CoV-2 spike protein, which could potentially make the liver cells targets for previously primed spike protein reactive cytotoxic T cells. There has been case reports on individuals who developed autoimmune hepatitis [39] after BNT162b2 vaccination. To obtain better understanding of the potential effects of BNT162b2 on liver function, in vivo models are desired for future studies.
In the BNT162b2 toxicity report, no genotoxicity nor carcinogenicity studies have been provided [26]. Our study shows that BNT162b2 can be reverse transcribed to DNA in liver cell line Huh7, and this may give rise to the concern if BNT162b2-derived DNA may be integrated into the host genome and affect the integrity of genomic DNA, which may potentially mediate genotoxic side effects. At this stage, we do not know if DNA reverse transcribed from BNT162b2 is integrated into the cell genome. Further studies are needed to demonstrate the effect of BNT162b2 on genomic integrity, including whole genome sequencing of cells exposed to BNT162b2, as well as tissues from human subjects who received BNT162b2 vaccination.
Human autonomous retrotransposon LINE-1 is a cellular endogenous reverse transcriptase and the only remaining active transposon in humans, able to retrotranspose itself and other nonautonomous elements [40,41], and ~17% of the human genome are comprised of LINE-1 sequences [42]. The nonautonomous Alu elements, short, interspersed nucleotide elements (SINEs), variable-number-of-tandem-repeats (VNTR), as well as cellular mRNA-processed pseudogenes, are retrotransposed by the LINE-1 retrotransposition proteins working in trans [43,44]. A recent study showed that endogenous LINE-1 mediates reverse transcription and integration of SARS-CoV-2 sequences in the genomes of infected human cells [25]. Furthermore, expression of endogenous LINE-1 is often increased upon viral infection, including SARS-CoV-2 infection [45,46,47]. Previous studies showed that LINE-1 retrotransposition activity is regulated by RNA metabolism [48,49], DNA damage response [50], and autophagy [51]. Efficient retrotransposition of LINE-1 is often associated with cell cycle and nuclear envelope breakdown during mitosis [52,53], as well as exogenous retroviruses [54,55], which promotes entrance of LINE-1 into the nucleus. In our study, we observed increased LINE-1 ORF1p distribution as determined by immunohistochemistry in the nucleus by BNT162b2 at all concentrations tested (0.5, 1, and 2 μg/mL), while elevated LINE-1 gene expression was detected at the highest BNT162b2 concentration (2 μg/mL). It is worth noting that gene transcription is regulated by chromatin modifications, transcription factor regulation, and the rate of RNA degradation, while translational regulation of protein involves ribosome recruitment on the initiation codon, modulation of peptide elongation, termination of protein synthesis, or ribosome biogenesis. These two processes are controlled by different mechanisms, and therefore they may not always show the same change patterns in response to external challenges. The exact regulation of LINE-1 activity in response to BNT162b2 merits further study.
The cell model that we used in this study is a carcinoma cell line, with active DNA replication which differs from non-dividing somatic cells. It has also been shown that Huh7 cells display significant different gene and protein expression including upregulated proteins involved in RNA metabolism [56]. However, cell proliferation is also active in several human tissues such as the bone marrow or basal layers of epithelia as well as during embryogenesis, and it is therefore necessary to examine the effect of BNT162b2 on genomic integrity under such conditions. Furthermore, effective retrotransposition of LINE-1 has also been reported in non-dividing and terminally differentiated cells, such as human neurons [57,58].
The Pfizer EMA assessment report also showed that BNT162b2 distributes in the spleen (<1.1%), adrenal glands (<0.1%), as well as low and measurable radioactivity in the ovaries and testes (<0.1%) [26]. Furthermore, no data on placental transfer of BNT162b2 is available from Pfizer EMA assessment report. Our results showed that BNT162b2 mRNA readily enters Huh7 cells at a concentration (0.5 µg/mL) corresponding to 0.5% of the local injection site concentration, induce changes in LINE-1 gene and protein expression, and within 6 h, reverse transcription of BNT162b2 can be detected. It is therefore important to investigate further the effect of BNT162b2 on other cell types and tissues both in vitro and in vivo.
5. Conclusions
Our study is the first in vitro study on the effect of COVID-19 mRNA vaccine BNT162b2 on human liver cell line. We present evidence on fast entry of BNT162b2 into the cells and subsequent intracellular reverse transcription of BNT162b2 mRNA into DNA.
Supplementary Materials
The following supporting information can be downloaded at: https://www.mdpi.com/article/10.3390/cimb44030073/s1.
Author Contributions
M.A., F.O.F., D.Y., M.B. and C.L. performed in vitro experiments. M.A. and F.O.F. performed data analysis. M.R. and Y.D.M. contributed to the implementation of the research, designed, and supervised the study. Y.D.M. wrote the paper with input from all authors. All authors have read and agreed to the published version of the manuscript.
Funding
This study was supported by the Swedish Research Council, Strategic Research Area Exodiab, Dnr 2009-1039, the Swedish Government Fund for Clinical Research (ALF) and the foundation of Skåne University Hospital.
Institutional Review Board Statement
Not applicable.
Informed Consent Statement
Not applicable.
Data Availability Statement
All data supporting the findings of this study are available within the article and supporting information.
Acknowledgments
The authors thank Sven Haidl, Maria Josephson, Enming Zhang, Jia-Yi Li, Caroline Haikal, and Pradeep Bompada for their support to this study.
Conflicts of Interest
The authors declare no conflict of interest.
References
- World Health Organization. Coronavirus (COVID-19) Dashboard. Available online: https://covid19.who.int/ (accessed on 22 February 2022).
- Mulligan, M.J.; Lyke, K.E.; Kitchin, N.; Absalon, J.; Gurtman, A.; Lockhart, S.; Neuzil, K.; Raabe, V.; Bailey, R.; Swanson, K.A.; et al. Phase I/II study of COVID-19 RNA vaccine BNT162b1 in adults. Nature 2020, 586, 589–593. [Google Scholar] [CrossRef] [PubMed]
- Walsh, E.E.; Frenck, R.W., Jr.; Falsey, A.R.; Kitchin, N.; Absalon, J.; Gurtman, A.; Lockhart, S.; Neuzil, K.; Mulligan, M.J.; Bailey, R.; et al. Safety and Immunogenicity of Two RNA-Based COVID-19 Vaccine Candidates. N. Engl. J. Med. 2020, 383, 2439–2450. [Google Scholar] [CrossRef] [PubMed]
- Polack, F.P.; Thomas, S.J.; Kitchin, N.; Absalon, J.; Gurtman, A.; Lockhart, S.; Perez, J.L.; Perez Marc, G.; Moreira, E.D.; Zerbini, C.; et al. Safety and Efficacy of the BNT162b2 mRNA COVID-19 Vaccine. N. Engl. J. Med. 2020, 383, 2603–2615. [Google Scholar] [CrossRef] [PubMed]
- Harris, R.J.; Hall, J.A.; Zaidi, A.; Andrews, N.J.; Dunbar, J.K.; Dabrera, G. Effect of Vaccination on Household Transmission of SARS-CoV-2 in England. N. Engl. J. Med. 2021, 385, 759–760. [Google Scholar] [CrossRef]
- Butt, A.A.; Omer, S.B.; Yan, P.; Shaikh, O.S.; Mayr, F.B. SARS-CoV-2 Vaccine Effectiveness in a High-Risk National Population in a Real-World Setting. Ann. Intern. Med. 2021, 174, 1404–1408. [Google Scholar] [CrossRef]
- Dagan, N.; Barda, N.; Kepten, E.; Miron, O.; Perchik, S.; Katz, M.A.; Hernan, M.A.; Lipsitch, M.; Reis, B.; Balicer, R.D. BNT162b2 mRNA Covid-19 Vaccine in a Nationwide Mass Vaccination Setting. N. Engl. J. Med. 2021, 384, 1412–1423. [Google Scholar] [CrossRef]
- Rossman, H.; Shilo, S.; Meir, T.; Gorfine, M.; Shalit, U.; Segal, E. COVID-19 dynamics after a national immunization program in Israel. Nat. Med. 2021, 27, 1055–1061. [Google Scholar] [CrossRef]
- Fan, B.E.; Shen, J.Y.; Lim, X.R.; Tu, T.M.; Chang, C.C.R.; Khin, H.S.W.; Koh, J.S.; Rao, J.P.; Lau, S.L.; Tan, G.B.; et al. Cerebral venous thrombosis post BNT162b2 mRNA SARS-CoV-2 vaccination: A black swan event. Am. J. Hematol. 2021, 96, E357–E361. [Google Scholar] [CrossRef]
- Larson, K.F.; Ammirati, E.; Adler, E.D.; Cooper, L.T., Jr.; Hong, K.N.; Saponara, G.; Couri, D.; Cereda, A.; Procopio, A.; Cavalotti, C.; et al. Myocarditis After BNT162b2 and mRNA-1273 Vaccination. Circulation 2021, 144, 506–508. [Google Scholar] [CrossRef]
- Menni, C.; Klaser, K.; May, A.; Polidori, L.; Capdevila, J.; Louca, P.; Sudre, C.H.; Nguyen, L.H.; Drew, D.A.; Merino, J.; et al. Vaccine side-effects and SARS-CoV-2 infection after vaccination in users of the COVID Symptom Study app in the UK: A prospective observational study. Lancet Infect. Dis. 2021, 21, 939–949. [Google Scholar] [CrossRef]
- Hansen, T.; Titze, U.; Kulamadayil-Heidenreich, N.S.A.; Glombitza, S.; Tebbe, J.J.; Rocken, C.; Schulz, B.; Weise, M.; Wilkens, L. First case of postmortem study in a patient vaccinated against SARS-CoV-2. Int. J. Infect. Dis. 2021, 107, 172–175. [Google Scholar] [CrossRef] [PubMed]
- Kadali, R.A.K.; Janagama, R.; Peruru, S.; Malayala, S.V. Side effects of BNT162b2 mRNA COVID-19 vaccine: A randomized, cross-sectional study with detailed self-reported symptoms from healthcare workers. Int. J. Infect. Dis. 2021, 106, 376–381. [Google Scholar] [CrossRef] [PubMed]
- Parkash, O.; Sharko, A.; Farooqi, A.; Ying, G.W.; Sura, P. Acute Pancreatitis: A Possible Side Effect of COVID-19 Vaccine. Cureus 2021, 13, e14741. [Google Scholar] [CrossRef] [PubMed]
- Mazzatenta, C.; Piccolo, V.; Pace, G.; Romano, I.; Argenziano, G.; Bassi, A. Purpuric lesions on the eyelids developed after BNT162b2 mRNA COVID-19 vaccine: Another piece of SARS-CoV-2 skin puzzle? J. Eur. Acad. Dermatol. Venereol. 2021, 35, e543–e545. [Google Scholar] [CrossRef]
- Lee, E.J.; Cines, D.B.; Gernsheimer, T.; Kessler, C.; Michel, M.; Tarantino, M.D.; Semple, J.W.; Arnold, D.M.; Godeau, B.; Lambert, M.P.; et al. Thrombocytopenia following Pfizer and Moderna SARS-CoV-2 vaccination. Am. J. Hematol. 2021, 96, 534–537. [Google Scholar] [CrossRef]
- Ishay, Y.; Kenig, A.; Tsemach-Toren, T.; Amer, R.; Rubin, L.; Hershkovitz, Y.; Kharouf, F. Autoimmune phenomena following SARS-CoV-2 vaccination. Int. Immunopharmacol. 2021, 99, 107970. [Google Scholar] [CrossRef]
- Das, B.B.; Kohli, U.; Ramachandran, P.; Nguyen, H.H.; Greil, G.; Hussain, T.; Tandon, A.; Kane, C.; Avula, S.; Duru, C.; et al. Myopericarditis following mRNA COVID-19 Vaccination in Adolescents 12 through 18 Years of Age. J. Pediatr. 2021, 238, 26–32.e1. [Google Scholar] [CrossRef]
- McLaurin-Jiang, S.; Garner, C.D.; Krutsch, K.; Hale, T.W. Maternal and Child Symptoms Following COVID-19 Vaccination Among Breastfeeding Mothers. Breastfeed. Med. 2021, 16, 702–709. [Google Scholar] [CrossRef]
- Barda, N.; Dagan, N.; Ben-Shlomo, Y.; Kepten, E.; Waxman, J.; Ohana, R.; Hernan, M.A.; Lipsitch, M.; Kohane, I.; Netzer, D.; et al. Safety of the BNT162b2 mRNA Covid-19 Vaccine in a Nationwide Setting. N. Engl. J. Med. 2021, 385, 1078–1090. [Google Scholar] [CrossRef]
- Baden, L.R.; El Sahly, H.M.; Essink, B.; Kotloff, K.; Frey, S.; Novak, R.; Diemert, D.; Spector, S.A.; Rouphael, N.; Creech, C.B.; et al. Efficacy and Safety of the mRNA-1273 SARS-CoV-2 Vaccine. N. Engl. J. Med. 2021, 384, 403–416. [Google Scholar] [CrossRef]
- Sadoff, J.; Gray, G.; Vandebosch, A.; Cardenas, V.; Shukarev, G.; Grinsztejn, B.; Goepfert, P.A.; Truyers, C.; Fennema, H.; Spiessens, B.; et al. Safety and Efficacy of Single-Dose Ad26.COV2.S Vaccine against Covid-19. N. Engl. J. Med. 2021, 384, 2187–2201. [Google Scholar] [CrossRef] [PubMed]
- Eichinger, S.; Warkentin, T.E.; Greinacher, A. Thrombotic Thrombocytopenia after ChAdOx1 nCoV-19 Vaccination. Reply. N. Engl. J. Med. 2021, 385, e11. [Google Scholar] [CrossRef] [PubMed]
- Doroftei, B.; Ciobica, A.; Ilie, O.D.; Maftei, R.; Ilea, C. Mini-Review Discussing the Reliability and Efficiency of COVID-19 Vaccines. Diagnostics 2021, 11, 579. [Google Scholar] [CrossRef]
- Zhang, L.; Richards, A.; Barrasa, M.I.; Hughes, S.H.; Young, R.A.; Jaenisch, R. Reverse-transcribed SARS-CoV-2 RNA can integrate into the genome of cultured human cells and can be expressed in patient-derived tissues. Proc. Natl. Acad. Sci. USA 2021, 118, e2105968118. [Google Scholar] [CrossRef] [PubMed]
- Available online: https://www.ema.europa.eu/en/documents/assessment-report/comirnaty-epar-public-assessment-report_en.pdf (accessed on 24 February 2022).
- Tanaka, H.; Takata, N.; Sakurai, Y.; Yoshida, T.; Inoue, T.; Tamagawa, S.; Nakai, Y.; Tange, K.; Yoshioka, H.; Maeki, M.; et al. Delivery of Oligonucleotides Using a Self-Degradable Lipid-Like Material. Pharmaceutics 2021, 13, 544. [Google Scholar] [CrossRef]
- Sedic, M.; Senn, J.J.; Lynn, A.; Laska, M.; Smith, M.; Platz, S.J.; Bolen, J.; Hoge, S.; Bulychev, A.; Jacquinet, E.; et al. Safety Evaluation of Lipid Nanoparticle-Formulated Modified mRNA in the Sprague-Dawley Rat and Cynomolgus Monkey. Vet. Pathol. 2018, 55, 341–354. [Google Scholar] [CrossRef]
- Sato, Y.; Matsui, H.; Yamamoto, N.; Sato, R.; Munakata, T.; Kohara, M.; Harashima, H. Highly specific delivery of siRNA to hepatocytes circumvents endothelial cell-mediated lipid nanoparticle-associated toxicity leading to the safe and efficacious decrease in the hepatitis B virus. J. Control. Release 2017, 266, 216–225. [Google Scholar] [CrossRef]
- Heidel, J.D.; Yu, Z.; Liu, J.Y.; Rele, S.M.; Liang, Y.; Zeidan, R.K.; Kornbrust, D.J.; Davis, M.E. Administration in non-human primates of escalating intravenous doses of targeted nanoparticles containing ribonucleotide reductase subunit M2 siRNA. Proc. Natl. Acad. Sci. USA 2007, 104, 5715–5721. [Google Scholar] [CrossRef]
- Available online: https://www.cvdvaccine-us.com/ (accessed on 24 February 2022).
- Available online: http://bridgeslab.sph.umich.edu/protocols/index.php/Preparation_of_Tail_Samples_(for_Genotyping) (accessed on 24 February 2022).
- Gallud, A.; Munson, M.J.; Liu, K.; Idstrom, A.; Barriga, H.M.; Tabaei, S.; Aliakbarinodehi, N.; Ojansivu, M.; Lubart, Q.; Doutch, J.J.; et al. Time evolution of PEG-shedding and serum protein coronation determines the cell uptake kinetics and delivery of lipid nanoparticle. bioRxiv 2021. [Google Scholar] [CrossRef]
- World Health Organization Messenger RNA Encoding the Full-Length SARS-CoV-2 Spike Glycoprotein. 2020. Available online: https://web.archive.org/web/20210105162941/https://mednet-communities.net/inn/db/media/docs/11889.doc (accessed on 24 February 2022).
- Mita, P.; Wudzinska, A.; Sun, X.; Andrade, J.; Nayak, S.; Kahler, D.J.; Badri, S.; LaCava, J.; Ueberheide, B.; Yun, C.Y.; et al. LINE-1 protein localization and functional dynamics during the cell cycle. Elife 2018, 7, e30058. [Google Scholar] [CrossRef]
- Sato, Y.; Kinami, Y.; Hashiba, K.; Harashima, H. Different kinetics for the hepatic uptake of lipid nanoparticles between the apolipoprotein E/low density lipoprotein receptor and the N-acetyl-d-galactosamine/asialoglycoprotein receptor pathway. J. Control. Release 2020, 322, 217–226. [Google Scholar] [CrossRef]
- Vogel, A.B.; Kanevsky, I.; Che, Y.; Swanson, K.A.; Muik, A.; Vormehr, M.; Kranz, L.M.; Walzer, K.C.; Hein, S.; Guler, A.; et al. BNT162b vaccines protect rhesus macaques from SARS-CoV-2. Nature 2021, 592, 283–289. [Google Scholar] [CrossRef] [PubMed]
- Bahl, K.; Senn, J.J.; Yuzhakov, O.; Bulychev, A.; Brito, L.A.; Hassett, K.J.; Laska, M.E.; Smith, M.; Almarsson, O.; Thompson, J.; et al. Preclinical and Clinical Demonstration of Immunogenicity by mRNA Vaccines against H10N8 and H7N9 Influenza Viruses. Mol. Ther. 2017, 25, 1316–1327. [Google Scholar] [CrossRef] [PubMed]
- Bril, F.; Al Diffalha, S.; Dean, M.; Fettig, D.M. Autoimmune hepatitis developing after coronavirus disease 2019 (COVID-19) vaccine: Causality or casualty? J. Hepatol. 2021, 75, 222–224. [Google Scholar] [CrossRef]
- Kazazian, H.H., Jr.; Moran, J.V. Mobile DNA in Health and Disease. N. Engl. J. Med. 2017, 377, 361–370. [Google Scholar] [CrossRef] [PubMed]
- Coffin, J.M.; Fan, H. The Discovery of Reverse Transcriptase. Annu. Rev. Virol. 2016, 3, 29–51. [Google Scholar] [CrossRef]
- Lander, E.S.; Linton, L.M.; Birren, B.; Nusbaum, C.; Zody, M.C.; Baldwin, J.; Devon, K.; Dewar, K.; Doyle, M.; FitzHugh, W.; et al. Initial sequencing and analysis of the human genome. Nature 2001, 409, 860–921. [Google Scholar] [CrossRef]
- Ostertag, E.M.; Goodier, J.L.; Zhang, Y.; Kazazian, H.H., Jr. SVA elements are nonautonomous retrotransposons that cause disease in humans. Am. J. Hum. Genet. 2003, 73, 1444–1451. [Google Scholar] [CrossRef]
- Hancks, D.C.; Kazazian, H.H., Jr. Active human retrotransposons: Variation and disease. Curr. Opin. Genet. Dev. 2012, 22, 191–203. [Google Scholar] [CrossRef]
- Jones, R.B.; Song, H.; Xu, Y.; Garrison, K.E.; Buzdin, A.A.; Anwar, N.; Hunter, D.V.; Mujib, S.; Mihajlovic, V.; Martin, E.; et al. LINE-1 retrotransposable element DNA accumulates in HIV-1-infected cells. J. Virol. 2013, 87, 13307–13320. [Google Scholar] [CrossRef]
- Macchietto, M.G.; Langlois, R.A.; Shen, S.S. Virus-induced transposable element expression up-regulation in human and mouse host cells. Life Sci. Alliance 2020, 3, e201900536. [Google Scholar] [CrossRef] [PubMed]
- Yin, Y.; Liu, X.Z.; He, X.; Zhou, L.Q. Exogenous Coronavirus Interacts With Endogenous Retrotransposon in Human Cells. Front. Cell Infect. Microbiol. 2021, 11, 609160. [Google Scholar] [CrossRef] [PubMed]
- Belancio, V.P.; Roy-Engel, A.M.; Deininger, P. The impact of multiple splice sites in human L1 elements. Gene 2008, 411, 38–45. [Google Scholar] [CrossRef] [PubMed]
- Dai, L.; Taylor, M.S.; O’Donnell, K.A.; Boeke, J.D. Poly(A) binding protein C1 is essential for efficient L1 retrotransposition and affects L1 RNP formation. Mol. Cell Biol. 2012, 32, 4323–4336. [Google Scholar] [CrossRef]
- Servant, G.; Streva, V.A.; Derbes, R.S.; Wijetunge, M.I.; Neeland, M.; White, T.B.; Belancio, V.P.; Roy-Engel, A.M.; Deininger, P.L. The Nucleotide Excision Repair Pathway Limits L1 Retrotransposition. Genetics 2017, 205, 139–153. [Google Scholar] [CrossRef]
- Guo, H.; Chitiprolu, M.; Gagnon, D.; Meng, L.; Perez-Iratxeta, C.; Lagace, D.; Gibbings, D. Autophagy supports genomic stability by degrading retrotransposon RNA. Nat. Commun. 2014, 5, 5276. [Google Scholar] [CrossRef]
- Xie, Y.; Mates, L.; Ivics, Z.; Izsvak, Z.; Martin, S.L.; An, W. Cell division promotes efficient retrotransposition in a stable L1 reporter cell line. Mob. DNA 2013, 4, 10. [Google Scholar] [CrossRef]
- Shi, X.; Seluanov, A.; Gorbunova, V. Cell divisions are required for L1 retrotransposition. Mol. Cell Biol. 2007, 27, 1264–1270. [Google Scholar] [CrossRef]
- Goff, S.P. Host factors exploited by retroviruses. Nat. Rev. Microbiol 2007, 5, 253–263. [Google Scholar] [CrossRef]
- Suzuki, Y.; Craigie, R. The road to chromatin—Nuclear entry of retroviruses. Nat. Rev. Microbiol. 2007, 5, 187–196. [Google Scholar] [CrossRef]
- Shi, J.; Wang, X.; Lyu, L.; Jiang, H.; Zhu, H.J. Comparison of protein expression between human livers and the hepatic cell lines HepG2, Hep3B, and Huh7 using SWATH and MRM-HR proteomics: Focusing on drug-metabolizing enzymes. Drug Metab. Pharmacokinet. 2018, 33, 133–140. [Google Scholar] [CrossRef] [PubMed]
- Kubo, S.; Seleme, M.C.; Soifer, H.S.; Perez, J.L.; Moran, J.V.; Kazazian, H.H., Jr.; Kasahara, N. L1 retrotransposition in nondividing and primary human somatic cells. Proc. Natl. Acad. Sci. USA 2006, 103, 8036–8041. [Google Scholar] [CrossRef] [PubMed]
- Macia, A.; Widmann, T.J.; Heras, S.R.; Ayllon, V.; Sanchez, L.; Benkaddour-Boumzaouad, M.; Munoz-Lopez, M.; Rubio, A.; Amador-Cubero, S.; Blanco-Jimenez, E.; et al. Engineered LINE-1 retrotransposition in nondividing human neurons. Genome Res. 2017, 27, 335–348. [Google Scholar] [CrossRef] [PubMed]
|
Publisher’s Note: MDPI stays neutral with regard to jurisdictional claims in published maps and institutional affiliations.
|

Πρόσφατα Σχόλια